Orthomyxoviridae -Orthomyxoviridae
| Orthomyxoviridae | |
|---|---|
|
|
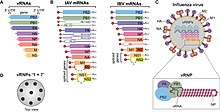
| Influenza A og influenza B viruses genom, mRNA og virion diagram | |
|
Virusklassificering |
|
| (uden rangering): | Virus |
| Rige : | Riboviria |
| Kongerige: | Orthornavirae |
| Phylum: | Negarnaviricota |
| Klasse: | Insthoviricetes |
| Bestille: | Articulavirales |
| Familie: | Orthomyxoviridae |
| Slægter | |
Orthomyxoviridae (fra græsk ὀρθός, orthós 'straight' + μύξα, mýxa ' mucus ') er en familie af RNA-vira med negativ sans . Det omfatter syv slægter : Alphainfluenzavirus , Betainfluenzavirus , Deltainfluenzavirus , Gammainfluenzavirus , Isavirus , Thogotovirus og Quaranjavirus . De første fire slægter indeholder vira, der forårsager influenza hos fugle (se også fugleinfluenza ) og pattedyr , herunder mennesker. Isavirus inficerer laks ; thogotovirus er arbovirus , inficerer hvirveldyr og hvirvelløse dyr (såsom flåter og myg ). Quaranjavirus er også arbovirus, der inficerer hvirveldyr (fugle) og hvirvelløse dyr ( leddyr ).
De fire slægter af influenzavirus, der inficerer hvirveldyr, som identificeres ved antigene forskelle i deres nukleoprotein og matrixprotein , er som følger:
- Alphainfluenzavirus inficerer mennesker, andre pattedyr og fugle og forårsager alle influenzapandemier
- Betainfluenzavirus inficerer mennesker og sæler
- Gammainfluenzavirus inficerer mennesker, svin og hunde
- Deltainfluenzavirus inficerer svin og kvæg .
Struktur
Den influenzavirus virionet er pleomorfe ; den virale kappe kan forekomme i sfæriske og filamentøse former. Generelt er virusets morfologi ellipsoid med partikler 100-120 nm i diameter eller filamentøse med partikler 80-100 nm i diameter og op til 20 µm lange. Der er cirka 500 forskellige pigge-lignende overfladefremspring i konvolutten, der hver projekterer 10-14 nm fra overfladen med varierende overfladetætheder. Den store glykoprotein (HA) pigg er indlagt uregelmæssigt af klynger af neuraminidase (NA) pigge, med et forhold mellem HA og NA på ca. 10 til 1.
Viralhylsteret sammensat af en lipid dobbeltlagsmembran , hvor glycoproteinspidserne er forankret, omslutter nukleocapsiderne ; nukleoproteiner af forskellige størrelsesklasser med en sløjfe i hver ende; arrangementet i virionen er usikkert. De ribonukleære proteiner er trådformede og falder i området 50-130 nm lange og 9-15 nm i diameter med spiralformet symmetri.
Genom

Virus af familien Orthomyxoviridae indeholder seks til otte segmenter af lineær negativ-sanset enkeltstrenget RNA. De har en samlet genomlængde, der er 10.000–14.600 nukleotider (nt). Influenza A- genomet har for eksempel otte stykker segmenteret negativ sanset RNA (i alt 13,5 kilobaser).
De bedst karakteriserede af influenzavirusproteinerne er hæmagglutinin og neuraminidase , to store glycoproteiner, der findes på ydersiden af viruspartiklerne. Hemagglutinin er et lektin, der medierer binding af viruset til målceller og indtræden af det virale genom i målcellen. I modsætning hertil er neuraminidase et enzym, der er involveret i frigivelsen af afkomvirus fra inficerede celler ved at spalte sukker, der binder de modne viruspartikler. Hæmagglutinin (H) og neuraminidase (N) proteiner er centrale mål for antistoffer og antivirale lægemidler, og de bruges til at klassificere de forskellige serotyper af influenza A -vira, deraf H og N i H5N1 .
Genom -sekvensen har terminale gentagne sekvenser; gentaget i begge ender. Terminal gentages ved 5′-enden 12-13 nukleotider lange. Nukleotidsekvenser af 3'-terminus identiske; det samme i slægter af samme familie; mest på RNA (segmenter) eller på alle RNA -arter. Terminal gentages ved 3′-enden 9-11 nukleotider lang. Indkapslet nukleinsyre er udelukkende genomisk. Hver virion kan indeholde defekte forstyrrende kopier. Ved influenza A (H1N1) produceres PB1-F2 fra en alternativ læseramme i PB1. M- og NS -generne producerer to forskellige gener via alternativ splejsning .
Replikationscyklus
Typisk overføres influenza fra inficerede pattedyr gennem luften ved hoste eller nys, hvilket skaber aerosoler, der indeholder viruset, og fra inficerede fugle gennem deres affald . Influenza kan også overføres af spyt , næsesekretion , afføring og blod . Infektioner opstår ved kontakt med disse kropsvæsker eller med forurenede overflader. Ud af en vært kan influenzavirus forblive smitsomme i cirka en uge ved menneskelig kropstemperatur, over 30 dage ved 0 ° C (32 ° F) og på ubestemt tid ved meget lave temperaturer (såsom søer i det nordøstlige Sibirien ). De kan let inaktiveres af desinfektionsmidler og rengøringsmidler .
Viraerne binder sig til en celle gennem interaktioner mellem dets hæmagglutininglycoprotein og sialinsyresukker på overflader af epitelceller i lunge og hals (trin 1 i infektionsfigur). Cellen importerer virussen ved endocytose . I det sure endosom fusionerer en del af hæmagglutininproteinet viralhylsteret med vakuolens membran og frigiver de virale RNA (vRNA) molekyler, tilbehørsproteiner og RNA-afhængig RNA-polymerase til cytoplasmaet (trin 2). Disse proteiner og vRNA danner et kompleks, der transporteres ind i cellekernen , hvor den RNA-afhængige RNA-polymerase begynder at transkribere komplementær positiv sans-cRNA (trin 3a og b). CRNA eksporteres enten til cytoplasmaet og translateres (trin 4) eller forbliver i kernen. Nyligt syntetiserede virale proteiner udskilles enten gennem Golgi -apparatet på celleoverfladen (i tilfælde af neuraminidase og hæmagglutinin, trin 5b) eller transporteres tilbage til kernen for at binde vRNA og danne nye virale genompartikler (trin 5a). Andre virale proteiner har flere handlinger i værtscellen, herunder nedbrydning af cellulært mRNA og anvendelse af de frigivne nukleotider til vRNA-syntese og inhiberer også translation af værtscelle-mRNA'er.
Negativ sans-vRNA'er, der danner genomer for fremtidige vira, RNA-afhængig RNA-transkriptase og andre virale proteiner, samles til en virion. Hemagglutinin og neuraminidase -molekyler klynger sig sammen til en bule i cellemembranen. VRNA og virale kerneproteiner forlader kernen og kommer ind i dette membranfremspring (trin 6). Den modne virus spirer af fra cellen i en sfære af værtsphospholipidmembran og erhverver hæmagglutinin og neuraminidase med denne membranbelægning (trin 7). Som før klæber vira til cellen gennem hæmagglutinin; de modne vira løsner sig, når deres neuraminidase har spaltet sialinsyrerester fra værtscellen. Efter frigivelsen af ny influenzavirus dør værtscellen.

Orthomyxoviridae -vira er en af to RNA -vira, der replikerer i kernen (den anden er retroviridae ). Det skyldes, at orthomyxo -virussystemer ikke kan lave deres egne mRNA'er. De bruger cellulære RNA'er som primere til at starte den virale mRNA -syntese i en proces kendt som cap -snapping . Når den er kommet ind i kernen, finder RNA Polymerase Protein PB2 et cellulært præ-mRNA og binder sig til dets 5 ′ tilsluttede ende. Derefter spaltes RNA Polymerase PA fra det cellulære mRNA nær 5' -enden og bruger dette lukkede fragment som en primer til transskribering af resten af det virale RNA -genom i viralt mRNA. Dette skyldes behovet for mRNA for at have en 5 ′ cap for at blive genkendt af cellens ribosom til translation.
Da RNA- korrekturlæsningsenzymer er fraværende, foretager den RNA-afhængige RNA-transkriptase en enkelt nukleotid-indsættelsesfejl omtrent hvert 10. tusinde nukleotider, hvilket er den omtrentlige længde af influenza-vRNA. Derfor vil næsten hver nyfremstillet influenzavirus indeholde en mutation i sit genom. Adskillelsen af genomet i otte separate segmenter af vRNA tillader blanding ( genassortering ) af generne, hvis mere end én variant af influenzavirus har inficeret den samme celle ( superinfektion ). Den resulterende ændring i genomsegmenterne pakket i virale afkom giver ny adfærd, undertiden evnen til at inficere nye værtsarter eller at overvinde værtspopulationernes beskyttende immunitet over for dets gamle genom (i så fald kaldes det et antigent skift ).
Klassifikation
I en fylogenetisk -baseret taksonomi inkluderer kategorien RNA -virus underkategorien negativ -sans ssRNA -virus , som omfatter ordenen Articulavirales og familien Orthomyxoviridae . De slægtsassocierede arter og serotyper af Orthomyxoviridae er vist i følgende tabel.
| Slægt | Arter (* angiver typearter ) | Serotyper eller undertyper | Værter |
|---|---|---|---|
| Alphainfluenzavirus | Influenza A -virus * | H1N1 , H1N2 , H2N2 , H3N1 , H3N2 , H3N8 , H5N1 , H5N2 , H5N3 , H5N8 , H5N9 , H7N1 , H7N2 , H7N3 , H7N4 , H7N7 , H7N9 , H9N2 , H10N7 | Menneske , gris , fugl , hest , flagermus |
| Betainfluenzavirus | Influenza B -virus * | Victoria, Yamagata | Menneske, sæl |
| Gammainfluenzavirus | Influenza C -virus * | Menneske, gris, hund | |
| Deltainfluenzavirus | Influenza D -virus * | Gris, kvæg | |
| Isavirus | Infektiøs lakseanæmi -virus * | Atlanterhavslaks | |
| Thogotovirus | Thogotovirus * | Flåt , myg , pattedyr (inklusive mennesker) | |
| Dhori -virus | Batken -virus , Bourbon -virus , Jos -virus | ||
| Quaranjavirus | |||
| Quaranfil -virus ,* Johnston Atoll -virus |
Typer
Der er fire slægter af influenzavirus, der hver kun indeholder en enkelt art eller type. Influenza A og C inficerer en række arter (inklusive mennesker), mens influenza B næsten udelukkende inficerer mennesker, og influenza D inficerer kvæg og svin.
Influenza A.
Influenza A -virus klassificeres yderligere baseret på de virale overfladeproteiner hemagglutinin (HA eller H) og neuraminidase (NA eller N). Seksten H -undertyper (eller serotyper) og ni N -undertyper af influenza A -virus er blevet identificeret.
Yderligere variation findes; specifikke influenzastammeisolater identificeres således ved en standardnomenklatur, der angiver virustype, geografisk placering, hvor den første isoleres, sekventielt antal isolationer, isolationsår og HA- og NA -undertype.
Eksempler på nomenklaturen er:
- A/Brisbane/59/2007 (H1N1)
- A/Moskva/10/99 (H3N2).
Type A -vira er de mest virulente humane patogener blandt de tre influenzatyper og forårsager den alvorligste sygdom. De serotyper, der er blevet bekræftet hos mennesker , sorteret efter antallet af kendte menneskelige pandemiske dødsfald, er:
- H1N1 forårsagede " spansk influenza " i 1918 og " svineinfluenza " i 2009.
- H2N2 forårsagede "asiatisk influenza".
- H3N2 forårsagede " Hong Kong Flu ".
- H5N1 , "aviær" eller "fugleinfluenza".
- H7N7 har usædvanligt zoonotisk potentiale.
- H1N2 inficerer svin og mennesker.
- H9N2 , H7N2 , H7N3 , H10N7 .
| Pandemiens navn | Dato | Dødsfald: Døde | Tilfælde af dødsfald i sager | Subtype involveret | Pandemisk sværhedsgrad |
|---|---|---|---|---|---|
|
1889-1890 influenzapandemi (asiatisk eller russisk influenza) |
1889–1890 | 1 million | 0,15% | Muligvis H3N8 eller H2N2 |
Ikke relevant |
|
1918 influenzapandemi (spansk influenza) |
1918–1920 | 20 til 100 mio | 2% | H1N1 | 5 |
| Asiatisk influenza | 1957–1958 | 1 til 1,5 mio | 0,13% | H2N2 | 2 |
| Hong Kong -influenza | 1968–1969 | 0,75 til 1 mio | <0,1% | H3N2 | 2 |
| Russisk influenza | 1977–1978 | Ingen præcis optælling | Ikke relevant | H1N1 | Ikke relevant |
| 2009 influenzapandemi | 2009–2010 | 105.700–395.600 | 0,03% | H1N1 | Ikke relevant |
Influenza B
Influenza B -virus er næsten udelukkende et humant patogen og er mindre almindeligt end influenza A. Det eneste andet dyr, der vides at være modtageligt for influenza B -infektion, er sælen . Denne type influenza muterer med en hastighed 2-3 gange lavere end type A og er derfor mindre genetisk forskelligartet, med kun én influenza B -serotype. Som et resultat af denne mangel på antigen diversitet opnås normalt en grad af immunitet over for influenza B i en tidlig alder. Influenza B muterer imidlertid nok til, at varig immunitet ikke er mulig. Denne reducerede antigeniske forandringshastighed kombineret med dets begrænsede værtsinterval (inhibering af antigenisk skift på tværs af arter ) sikrer, at pandemier af influenza B ikke forekommer.
Influenza C
Influenza C -virus inficerer mennesker og grise og kan forårsage alvorlig sygdom og lokale epidemier . Influenza C er imidlertid mindre almindelig end de andre typer og forårsager normalt mild sygdom hos børn.
Influenza D
Dette er en slægt, der blev klassificeret i 2016, hvis medlemmer først blev isoleret i 2011. Denne slægt ser ud til at være mest beslægtet med Influenza C, hvorfra den afviger for flere hundrede år siden. Der er mindst to eksisterende stammer af denne slægt. De vigtigste værter ser ud til at være kvæg, men virussen har også været kendt for at inficere svin.
Levedygtighed og desinfektion
Pattedyrs influenzavirus har en tendens til at være labile, men kan overleve flere timer i slim. Aviær influenzavirus kan overleve i 100 dage i destilleret vand ved stuetemperatur og 200 dage ved 17 ° C (63 ° F). Fuglevirussen inaktiveres hurtigere i husdyrgødning, men kan overleve i op til 2 uger i afføring på bur. Aviær influenzavirus kan overleve på ubestemt tid, når de er frosset. Influenzavirus er modtagelige for blegemiddel, 70% ethanol, aldehyder, oxidationsmidler og kvaternære ammoniumforbindelser. De inaktiveres ved varme på 133 ° F (56 ° C) i mindst 60 minutter samt ved lav pH <2.
Vaccination og profylakse
Vacciner og lægemidler er tilgængelige til profylakse og behandling af influenzavirusinfektioner. Vacciner består af enten inaktiverede eller levende svækkede virioner af H1N1 og H3N2 humane influenza A -vira samt influenza B -vira. Fordi antigeniciteterne hos de vilde vira udvikler sig, reformuleres vacciner årligt ved at opdatere frøstammerne.
Når frøstammernes og vilde virusses antigeniciteter ikke matcher, undlader vacciner at beskytte vaccinerne. Derudover genereres flugtmutanter ofte, selv når de matcher.
Lægemidler, der er tilgængelige til behandling af influenza, omfatter Amantadine og Rimantadine , som hæmmer virionsdækning ved at forstyrre M2, og Oseltamivir (markedsført under varemærket Tamiflu ), Zanamivir og Peramivir , som hæmmer frigivelse af virioner fra inficerede celler ved at interferere med NA. Imidlertid genereres flugtmutanter ofte for det tidligere lægemiddel og sjældnere for det sidste lægemiddel.
Se også
Referencer
Yderligere læsning
- Hoyle, L. (1969). Influenzavirus . Virologi monografier. 4 . Springer-Verlag. ISBN 978-3-211-80892-4. ISSN 0083-6591 . OCLC 4053391 .
eksterne links
- Health-EU Portal EU arbejder på at forberede et globalt svar på influenza.
- Influenza Research Database Database over influenza genomiske sekvenser og relateret information.
- Europa -Kommissionen - Folkesundhed EU -koordinering af pandemi (H1N1) 2009
- 3D Influenza-virus-relaterede strukturer fra EM Data Bank (EMDB)
- Viralzone : Orthomyxoviridae
- ICTV





