Alvorligt akut respiratorisk syndrom -relateret coronavirus -Severe acute respiratory syndrome–related coronavirus
| Alvorligt akut respiratorisk syndrom -relateret coronavirus | |
|---|---|

|
|
| Transmissionselektronmikrograf af SARS-relaterede coronavirus, der stammer fra værtsceller dyrket i laboratoriet | |
|
Virusklassificering |
|
| (uden rangering): | Virus |
| Rige : | Riboviria |
| Kongerige: | Orthornavirae |
| Phylum: | Pisuviricota |
| Klasse: | Pisoniviricetes |
| Bestille: | Nidovirales |
| Familie: | Coronaviridae |
| Slægt: | Betacoronavirus |
| Subgenus: | Sarbecovirus |
| Arter: |
Alvorligt akut respiratorisk syndrom -relateret coronavirus
|
| Stammer | |
|
|
| Synonymer | |
|
|
Alvorligt akut respiratorisk syndrom-relateret coronavirus ( SARSr-CoV eller SARS-CoV ) er en virusart, der består af mange kendte stammer fylogenetisk relateret til alvorligt akut respiratorisk syndrom coronavirus 1 (SARS-CoV-1), der har vist sig at have evnen at inficere mennesker , flagermus og visse andre pattedyr . Disse indhyllede , enkelt-strengede RNA-vira med positiv sans kommer ind i værtsceller ved at binde til den angiotensin-konverterende enzym 2 (ACE2) receptor. SARSr-CoV-arten er medlem af slægten Betacoronavirus og af undergenusen Sarbecovirus .
To stammer af virussen har forårsaget udbrud af alvorlige luftvejssygdomme hos mennesker: alvorligt akut respiratorisk syndrom coronavirus 1 (SARS-CoV eller SARS-CoV-1), som forårsagede 2002-2004 udbrud af alvorligt akut respiratorisk syndrom (SARS), og alvorligt akut respiratorisk syndrom coronavirus 2 (SARS-CoV-2), som forårsager den igangværende pandemi af COVID-19 . Der er hundredvis af andre stammer af SARSr-CoV, som kun vides at inficere ikke-menneskelige arter: flagermus er et stort reservoir af mange stammer af SARSr-CoV; adskillige stammer er blevet identificeret i håndflader , der sandsynligvis var forfædre til SARS-CoV-1.
Den SARS-relaterede coronavirus var en af flere vira, der blev identificeret af Verdenssundhedsorganisationen (WHO) i 2016 som en sandsynlig årsag til en fremtidig epidemi i en ny plan udviklet efter Ebola-epidemien til presserende forskning og udvikling før og under en epidemi mod diagnostik test , vacciner og medicin . Denne forudsigelse gik i opfyldelse i 2020 med COVID-19-pandemien .
Klassifikation
SARS-relateret coronavirus er medlem af slægten Betacoronavirus (gruppe 2) og monotypisk for underslægten Sarbecovirus (undergruppe B). Sarbecovirus har, i modsætning til embecovirus eller alphacoronavirus , kun en papainlignende proteinase ( PLpro ) i stedet for to i den åbne læseramme ORF1. SARSr-CoV var fast besluttet på at være en tidlig opdeling fra betacoronaviruset baseret på et sæt bevarede domæner, som den deler med gruppen.
Flagermus fungerer som den vigtigste værtsreservoirart for de SARS-relaterede coronavirus som SARS-CoV-1 og SARS-CoV-2. Virussen har coevolved sig i flagermusværtsreservoiret over en lang periode. Først for nylig er det blevet observeret, at stammer af SARS-relateret coronavirus har udviklet sig til at have været i stand til at få tværartene til at hoppe fra flagermus til mennesker, som for stammerne SARS-CoV og SARS-CoV-2 . Begge disse stammer stammede fra en enkelt forfader, men fik krydsarten til at hoppe ind i mennesker hver for sig. SARS-CoV-2 er ikke en direkte efterkommer af SARS-CoV.
Genom
Den SARS-relaterede coronavirus er en indhyllet, positivt sanset, enkeltstrenget RNA-virus . Dens genom er omkring 30 kb , hvilket er et af de største blandt RNA -vira. Virussen har 14 åbne læserammer, der i nogle tilfælde overlapper hinanden. Genomet har den sædvanlige 5 ′ methylerede hætte og en 3 ′ polyadenyleret hale . Der er 265 nukleotider i 5'UTR og 342 nukleotider i 3'UTR .
5 'methyleret hætte og 3' polyadenyleret hale gør det muligt for RNA-genomet med positiv sans at blive translateret direkte af værtscellens ribosom ved viral indgang . SARSr-CoV ligner andre coronavirus, idet dets genomekspression starter med translation af værtscellens ribosomer af de første to store overlappende åbne læserammer (ORF'er), 1a og 1b, som begge producerer polyproteiner .
| Funktion af SARS-CoV genomproteiner (orf1a til orf9b) |
|
|---|---|
| Protein | Fungere |
| orf1ab P0C6X7 |
Replicase/transcriptase polyprotein (pp1ab) ( ikke -strukturelle proteiner ) |
| orf2 P59594 |
Spike (S) protein, virusbinding og indtræden ( strukturelt protein ) |
|
orf3a P59632 |
Interagerer med S, E, M strukturelle proteiner; Ionkanalaktivitet ; Opregulerer cytokiner og kemokiner, såsom IL-8 og RANTES ; Opregulerer NF-κB og JNK ; Fremkalder apoptose og cellecyklusstop via Caspase 8 og -9 , og af Bax , p53 og p38 MAP kinase |
| orf3b P59633 |
Opregulerer cytokiner og kemokiner med RUNX1b ; Hæmmer produktion og signalering af type I IFN ; Fremkalder apoptose og cellecyklusstop ; |
| ORF4 P59637 |
Envelope (E) protein, virussamling og spirende ( strukturelt protein ) |
| ORF5 P59596 |
Membran (M) protein, virussamling og spirende ( strukturelt protein ) |
| orf6 P59634 |
Forbedrer cellulær DNA -syntese; Hæmmer produktion og signalering af type I IFN |
|
orf7a P59635 |
Hæmmer cellulær proteinsyntese; Fremkalder inflammatorisk respons af NF-kappaB og IL-8 promotor ; Opreguler kemokiner såsom IL-8 og RANTES; Opregulerer JNK, p38 MAP kinase; Fremkalder apoptose og cellecyklusstop |
| orf7b Q7TFA1 |
Ukendt |
| orf8a Q7TFA0 |
Inducerer apoptose gennem mitokondrier pathway |
| orf8b Q80H93 |
Forbedrer cellulær DNA -syntese, også kendt som X5. |
| orf9a P59595 |
Nucleocapsid (N) protein, viral RNA emballage ( strukturelt protein ) |
| orf9b P59636 |
Fremkalder apoptose |
| orf10 Q7TLC7 |
SARS-specifikt "protein 14" |
Funktionerne for flere af de virale proteiner er kendte. ORF'er la og 1b koder for replikase/transkriptasepolyproteinet og senere ORF'er 2, 4, 5 og 9a koder for henholdsvis de fire store strukturelle proteiner: pigge (S), kappe (E), membran (M) og nukleocapsid ( N). De senere ORF'er koder også for otte unikke proteiner (orf3a til orf9b), kendt som accessoriske proteiner, mange uden kendte homologer. Tilbehørsproteinernes forskellige funktioner er ikke godt forstået.
SARS -coronavirus er blevet genetisk manipuleret i flere laboratorier.
Filogenetik
Fylogenetisk analyse viste, at den evolutionære gren bestående af Bat coronavirus BtKY72 og BM48-31 var basegruppen af SARS-relaterede CoVs-evolutionære træer, som adskilte sig fra andre SARS-relaterede CoV'er tidligere end SARS-CoV-1 og SARS-CoV-2.
| SARSr -CoV |
|
||||||||||||||||||||||||||||||||||||||||||
Et fylogenetisk træ baseret på helgenomsekvenser af SARS-CoV-1 og relaterede coronavirus er:
| SARS -CoV -1 -relateret coronavirus |
|
|||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|
SARS-CoV-2 , 79% til SARS-CoV-1 |
||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Et fylogenetisk træ baseret på helgenomsekvenser af SARS-CoV-2 og relaterede coronavirus er:
| SARS -CoV -2 -relateret coronavirus |
|
||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|
SARS-CoV-1 , 79% til SARS-CoV-2 |
|||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Morfologi
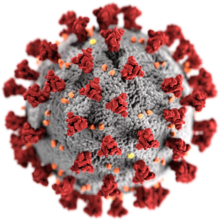

Morfologien for den SARS-relaterede coronavirus er karakteristisk for coronavirus-familien som helhed. Vira er store pleomorfe sfæriske partikler med løgformede overfladefremspring, der danner en corona omkring partiklerne i elektronmikrografer. Størrelsen af viruspartiklerne er i området 80–90 nm. Viruens konvolut i elektronmikrografer fremstår som et særskilt par elektrontætte skaller.
Den virale kappe består af et lipiddobbeltlag , hvor membranen (M), envelope (E) og spike (S) proteiner er forankret. Spike -proteinerne forsyner virussen med sine løgformede overfladefremspring. Spike -proteinets interaktion med dets komplement -værtscellereceptor er central for at bestemme vævets tropisme , infektivitet og artens rækkevidde af viruset.
Inde i konvolutten er der nucleocapsid , som er dannet af flere kopier af nucleocapsid (N) -proteinet, som er bundet til det positivt sansede enkeltstrengede (~ 30 kb ) RNA-genom i et kontinuerligt perler-på-a- streng type konformation. Lipidhylsteret, membranproteiner og nucleocapsid beskytter virussen, når den er uden for værten.
Livscyklus
SARS-relateret coronavirus følger den replikationsstrategi, der er typisk for alle coronavirus.
Vedhæftning og indgang
Vedhæftningen af den SARS-relaterede coronavirus til værtscellen medieres af piggproteinet og dets receptor. Spike-proteinreceptorbindingsdomænet (RBD) genkender og binder til den angiotensin-konverterende enzym 2 (ACE2) receptor. Efter vedhæftning kan virussen komme ind i værtscellen på to forskellige veje. Den vej, som virussen tager, afhænger af den værtsprotease , der er tilgængelig for at spalte og aktivere det receptor-tilknyttede pigprotein.
Den første vej, SARS -coronavirus kan gå for at komme ind i værtscellen, er ved endocytose og optagelse af virussen i et endosom . Receptor-bundet spikeprotein aktiveres derefter med værtens pH-afhængig cysteinprotease cathepsin L . Aktivering af det receptor-fastgjorte piggprotein forårsager en konformationsændring og den efterfølgende fusion af viralhylsteret med den endosomale væg .
Alternativt kan virusset ind i værtscellen direkte ved proteolytisk spaltning af receptoren-attached spikeprotein af værtens TMPRSS2 eller TMPRSS11D serinproteaser ved celleoverfladen. I SARS-coronavirus udløser aktiveringen af den C-terminale del af piggproteinet sammensmeltning af viralhylsteret med værtscellemembranen ved at inducere konformationsændringer, som ikke er fuldt ud forstået.
Oversættelse af genom
| Funktion af ikke -strukturelle proteiner i coronavirus (nsps) |
|
|---|---|
| Protein | Fungere |
| nsp1 | Fremmer vært mRNA nedbrydning, blokerer vært oversættelse ; blokerer medfødt immunrespons |
| nsp2 | Binder til prohibitin proteiner; ukendt funktion |
| nsp3 | Multidoman transmembranprotein ; interagerer med N -protein ; fremmer cytokinekspression ; PLPro -domæne spalter polyprotein pp1ab og blokerer værtens medfødte immunrespons; andre domæner ukendte funktioner |
| nsp4 | Transmembran stillads protein ; muliggør korrekt struktur til dobbeltmembranvesikler (DMV'er) |
| nsp5 | 3CLPro spalter polyprotein pp1ab |
| nsp6 | Transmembran stillads protein; ukendt funktion |
| nsp7 | Danner hexadecamerisk kompleks med nsp8; processivitetsklemme til RdRp (nsp12) |
| nsp8 | Danner hexadecamerisk kompleks med nsp7; processivitetsklemme til RdRp (nsp12); fungerer som en primase |
| nsp9 | RNA-bindende protein (RBP) |
| nsp10 | nsp16 og nsp14 cofaktor ; danner heterodimer med begge; stimulerer 2-O-MT (nsp16) og ExoN (nsp14) aktivitet |
| nsp11 | Ukendt funktion |
| nsp12 | RNA-afhængig RNA-polymerase (RdRp) |
| nsp13 | RNA helicase , 5 ′ trifosfatase |
| nsp14 | N7 Methyltransferase , 3'-5'exoribonuclease (ExoN); N7 MTase tilføjer 5 ′ cap , ExoN korrekturlæser genom |
| nsp15 | Endoribonuklease (NendoU) |
| nsp16 | 2'-O-methyltransferase (2-O-MT); beskytter viralt RNA mod MDA5 |
Efter fusion passerer nukleokapsidet ind i cytoplasmaet , hvor det virale genom frigives. Genom fungerer som et messenger-RNA , og cellens ribosom oversætter to tredjedele af genomet, som svarer til den åbne læseramme ORF1a og ORF1b, til to store overlappende polyproteiner, pp1a og pp1ab.
Det større polyprotein pp1ab er et resultat af et -1 ribosomalt rammeskift forårsaget af en glat sekvens (UUUAAAC) og et nedstrøms RNA -pseudoknot i slutningen af den åbne læseramme ORF1a. Det ribosomale rammeskift muliggør kontinuerlig translation af ORF1a efterfulgt af ORF1b.
Polyproteinerne indeholder deres egne proteaser , PLpro og 3CLpro , som spalter polyproteinerne på forskellige specifikke steder. Spaltningen af polyprotein pp1ab giver 16 ikke -strukturelle proteiner (nsp1 til nsp16). Produktproteiner omfatter forskellige replikationsproteiner, såsom RNA-afhængig RNA-polymerase (RdRp), RNA- helikase og exoribonuclease (ExoN).
De to SARS-CoV-2 proteaser (PLpro og 3CLpro) forstyrrer også immunsystemets reaktion på virusinfektionen ved at spalte tre immunsystemproteiner. PLpro spalter IRF3 og 3CLpro spalter både NLRP12 og TAB1 . "Direkte spaltning af IRF3 af NSP3 kunne forklare den afstumpede type-I IFN-reaktion, der blev set under SARS-CoV-2-infektioner, mens NSP5-medieret spaltning af NLRP12 og TAB1 peger på en molekylær mekanisme til forbedret produktion af IL-6 og inflammatorisk respons observeret i COVID -19 patienter. "
Replikation og transkription

Et antal af de ikke-strukturelle replikationsproteiner samles for at danne et multi-protein replikase-transkriptase-kompleks (RTC). Det vigtigste replikase-transkriptaseprotein er den RNA-afhængige RNA-polymerase (RdRp). Det er direkte involveret i replikation og transkription af RNA fra en RNA -streng. De andre ikke -strukturelle proteiner i komplekset hjælper med replikations- og transkriptionsprocessen.
Proteinet nsp14 er en 3'-5 'exoribonuclease, som giver ekstra troskab til replikationsprocessen. Exoribonucleasen tilvejebringer en korrekturfunktion til det kompleks, som den RNA-afhængige RNA-polymerase mangler. På samme måde danner proteiner nsp7 og nsp8 en hexadecamerisk glideklemme som en del af komplekset, hvilket i høj grad øger processiviteten af den RNA-afhængige RNA-polymerase. Corona -virusene kræver den øgede loyalitet og processivitet under RNA -syntese på grund af den relativt store genomstørrelse i sammenligning med andre RNA -vira.
En af hovedfunktionerne i replikase-transkriptase-komplekset er at transkribere det virale genom. RdRp formidler direkte syntesen af subgenomiske RNA-molekyler med negativ sans fra det genomiske RNA med positiv sans. Dette efterfølges af transkription af disse subgenomiske RNA-molekyler med negativ sans til deres tilsvarende positive sans- mRNA'er .
Den anden vigtige funktion af replikase-transkriptase-komplekset er at replikere det virale genom. RdRp formidler direkte syntesen af genomisk RNA med negativ sans fra det genomiske RNA med positiv sans. Dette efterfølges af replikationen af genomisk RNA med positiv sans fra det genomiske RNA med negativ sans.
Det replikerede genomiske RNA med positiv sans bliver genomet til virus afkom . De forskellige mindre mRNA'er er transkripter fra den sidste tredjedel af virusgenomet, der følger læserammerne ORF1a og ORF1b. Disse mRNA'er oversættes til de fire strukturelle proteiner (S, E, M og N), der vil blive en del af afkomviruspartiklerne og også otte andre accessoriske proteiner (orf3 til orf9b), som hjælper viruset.
Rekombination
Når to SARS-CoV- genomer er til stede i en værtscelle, kan de interagere med hinanden for at danne rekombinante genomer, der kan overføres til afkomvira. Rekombination forekommer sandsynligvis under genomreplikation, når RNA -polymerasen skifter fra en skabelon til en anden (rekombination af kopivalg). Human SARS-CoV ser ud til at have haft en kompleks rekombinationshistorie mellem forfædre coronavirus, der var vært i flere forskellige dyregrupper.
Montering og frigivelse
RNA -translation forekommer inde i det endoplasmatiske retikulum . De virale strukturelle proteiner S, E og M bevæger sig langs den sekretoriske vej ind i Golgi -mellemrummet . Der dirigerer M-proteinerne de fleste protein-protein-interaktioner, der kræves til samling af vira, efter dets binding til nucleocapsidet.
Afkomvira frigives fra værtscellen ved exocytose gennem sekretoriske vesikler.
Se også
- Bat SARS-lignende coronavirus WIV1 (SL-CoV-WIV1)
- Bat SARS-lignende coronavirus RsSHC014
- Flagermus coronavirus RaTG13
- Civet SARS-CoV
Noter
Referencer
Yderligere læsning
- Peiris JS, Lai ST, Poon LL, Guan Y, Yam LY, Lim W, et al. (April 2003). "Coronavirus som en mulig årsag til alvorligt akut respiratorisk syndrom" . Lancet . 361 (9366): 1319–25. doi : 10.1016/s0140-6736 (03) 13077-2 . PMC 7112372 . PMID 12711465 .
- Rota PA, Oberste MS, Monroe SS, Nix WA, Campagnoli R, Icenogle JP, et al. (Maj 2003). "Karakterisering af en ny coronavirus forbundet med alvorligt akut respiratorisk syndrom" . Videnskab . 300 (5624): 1394–9. Bibcode : 2003Sci ... 300.1394R . doi : 10.1126/science.1085952 . PMID 12730500 .
- Marra MA, Jones SJ, Astell CR, Holt RA, Brooks-Wilson A, Butterfield YS, et al. (Maj 2003). "Genomsekvensen af den SARS-associerede coronavirus" . Videnskab . 300 (5624): 1399–404. Bibcode : 2003Sci ... 300.1399M . doi : 10.1126/science.1085953 . PMID 12730501 .
- Snijder EJ, Bredenbeek PJ, Dobbe JC, Thiel V, Ziebuhr J, Poon LL, et al. (August 2003). "Unikke og bevarede træk ved genom og proteom af SARS-coronavirus, en tidlig opdeling fra coronavirus-gruppe 2-slægten" . Journal of Molecular Biology . 331 (5): 991–1004. CiteSeerX 10.1.1.319.7007 . doi : 10.1016/S0022-2836 (03) 00865-9 . PMC 7159028 . PMID 12927536 . S2CID 14974326 .
- Yount B, Roberts RS, Lindesmith L, Baric RS (august 2006). "Genopretning af det alvorlige akutte respiratoriske syndrom coronavirus (SARS-CoV) transkriptionskredsløb: konstruere et rekombinationsresistent genom" . Procedurer fra National Academy of Sciences i Amerikas Forenede Stater . 103 (33): 12546–51. Bibcode : 2006PNAS..10312546Y . doi : 10.1073/pnas.0605438103 . PMC 1531645 . PMID 16891412 .
- Thiel V, red. (2007). Coronaviruses: Molekylær og cellulær biologi (1. udgave). Caister Academic Press. ISBN 978-1-904455-16-5.
- Enjuanes L, Sola I, Zúñiga S, Almazán F (2008). "Coronavirus -replikation og interaktion med værten". I Mettenleiter TC, Sobrino F (red.). Dyrevirus: Molekylærbiologi . Caister Academic Press. ISBN 978-1-904455-22-6.
eksterne links
-
 Medier relateret til alvorlig akut respiratorisk syndrom-relateret coronavirus på Wikimedia Commons
Medier relateret til alvorlig akut respiratorisk syndrom-relateret coronavirus på Wikimedia Commons -
 Data relateret til alvorlig akut respiratorisk syndrom -relateret coronavirus på Wikispecies
Data relateret til alvorlig akut respiratorisk syndrom -relateret coronavirus på Wikispecies - WHO's pressemeddelelse, der identificerer og navngiver SARS -virussen
- SARS -virusets genetiske kort
- Speciel videnskab om SARS -virus (gratis indhold: ingen registrering nødvendig)
- McGill University SARS Resources på Wayback Machine (arkiveret 1. marts 2005)
- Amerikanske centre for sygdomsbekæmpelse og forebyggelse (CDC) SARS hjemme
- Verdenssundhedsorganisationen i alarmberedskab


